Bactéries du Corps Humain |
Bactéries : Elles Font se que Nous Sommes |



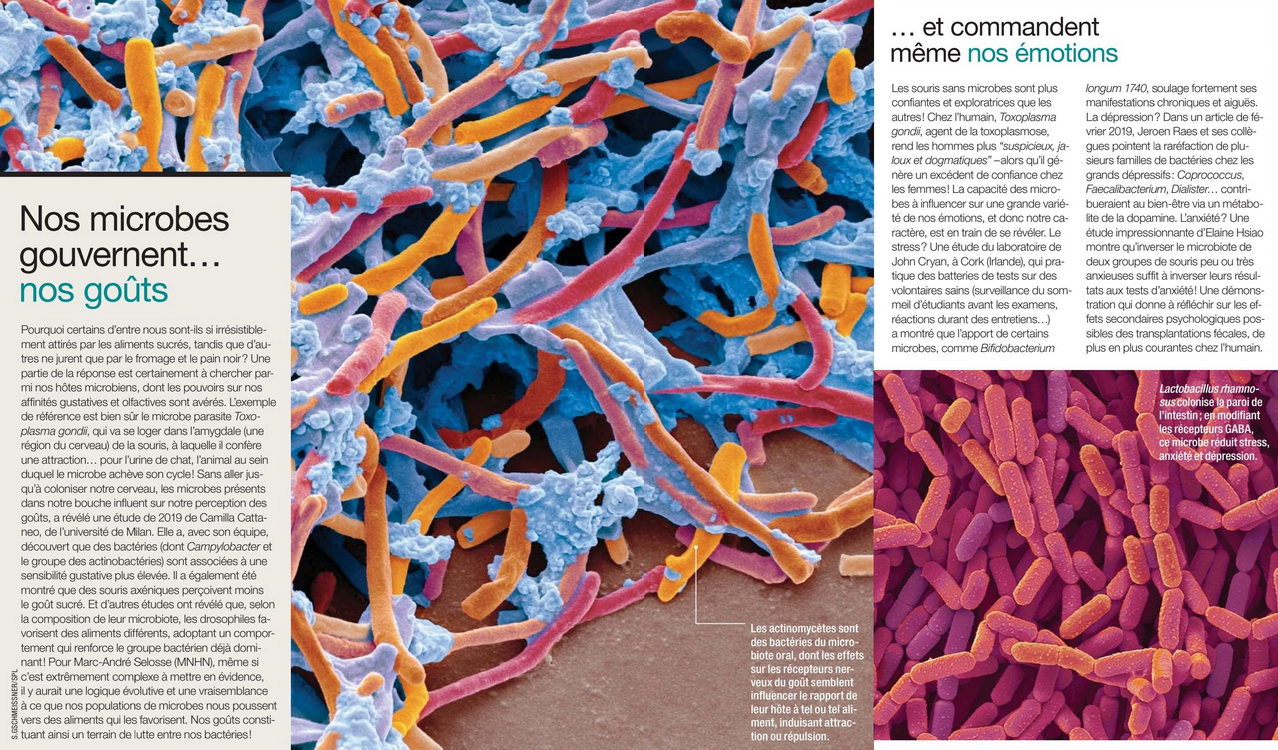



Y.S. - SCIENCE & VIE N°1240 > Janvier > 2021 |
|
À chacun son Nuage de Bactéries |

H.R. - SCIENCE ET AVENIR N°825 > Novembre > 2015 |
|
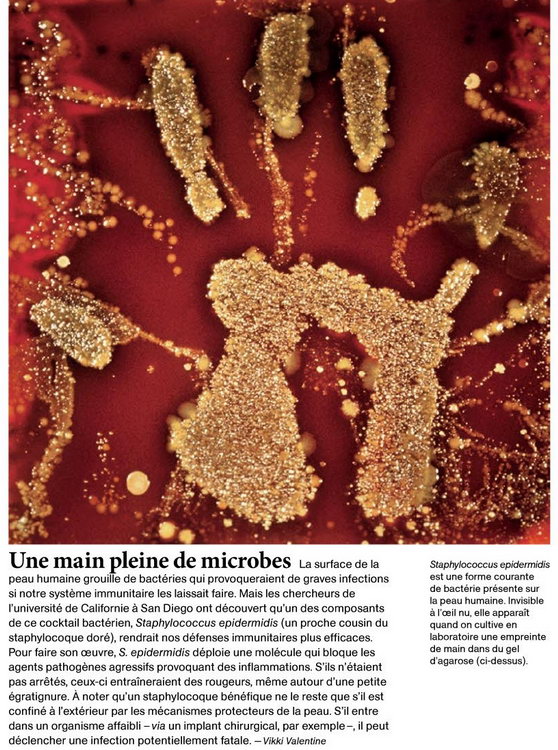
Une Main pleine de Microbes |
Connait-on le Poids Total des Bactéries dans notre Corps ? |

V.V. - NATIONAL GEOGRAPHIC N°174 > Mars > 2014 |
|
R.P. - SCIENCE & VIE QUESTIONS RÉPONSES N°12 > Juillet > 2014 |
Un Écosystème se Niche dans notre Nombril |
BACTÉRIOLOGIE |
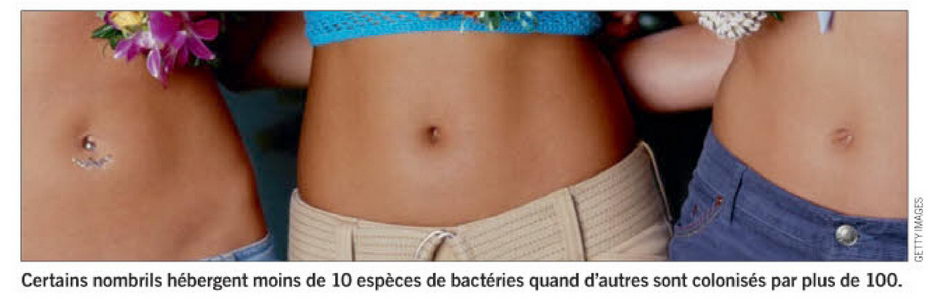 Notre nombril hèberge près de 2400 espèces de bacteries distinctes. Mieux encore, nous aurions chacun un mini-écosystème bien à nous, très différent de celui de notre voisin.
Notre nombril hèberge près de 2400 espèces de bacteries distinctes. Mieux encore, nous aurions chacun un mini-écosystème bien à nous, très différent de celui de notre voisin.
La moitié des espèces bactériennes sont présentes dans moins de 10 % des échantillons et souvent dans un seul d'entre eux. Telles sont les conclusions d'une équipe de l'université de Caroline du Nord, qui a recensé la diversité bactérienne dans le nombril d'une soixantaine de volontaires.
Poussant plus loin leur investigation, les chercheurs ont découvert que la diversité des écosystèmes ombilicaux varie beaucoup d'un individu à l'autre : certains hébergent moins de 10 espèces distinctes, alors que d'autres en ont plus d'une centaine, la moyenne se situant autour de 67. Ils ont même eu la surprise de recenser d'autres types de micro-organismes, des archées, chez quelqu'un qui ne s'était pas lavé le nombril depuis des années. Et chez un autre individu, ils ont découvert une bacterie très rare, seulement connue jusqu'à présent dans le sol japonais ! C'est lors d'une conférence scientifique grand public, que les chercheurs américains ont eu lidée de s'intéresser à l'écologie du nombril. Grâce à un site Internet, ils ont recueilli plus de 2000 échantillons. Sans trop savoir ce qu'ils pourront tirer comme conclusion de leur étude, ils maintiennent leur appel aux dons.
E.G. - SCIENCES ET AVENIR N°791 > Janvier > 2013 |
|
Pourrions-nous Exister Sans Bactéries ? |
BACTÉRIOLOGIE |
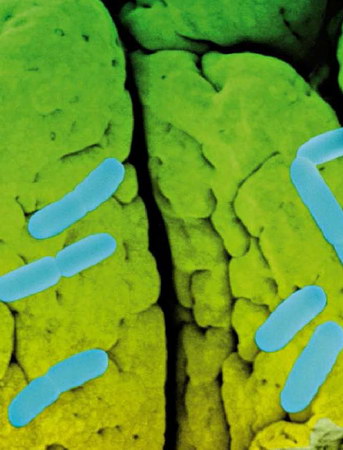 Non, on peut même dire que les bactéries (certaines tout du moins) sont les meilleures amies de l'homme : notre corps en contient 10 fois plus que de cellules humaines.
Non, on peut même dire que les bactéries (certaines tout du moins) sont les meilleures amies de l'homme : notre corps en contient 10 fois plus que de cellules humaines.
Il s'agit d'organismes vivants extrêmement rudimentaires (en substance, des cellules dépourvues de noyau) et minuscules : elles sont en moyenne 10 fois plus petites que les cellules humaines. Surtout, elles ont le don de tout coloniser, et notamment notre organisme, où elles se trouvent partout : dans l'appareil digestif, la peau, les yeux, le nez, les muqueuses...
Au vrai, ce sont plusieurs milliers d'espèces de bactéries qui élisent domicile dans notre corps. Exception faite des bactéries pathogènes responsables des maladies infectieuses, la plupart sont inoffensives... et nombreuses sont celles qui s'avèrent bénéfiques en constituant de véritables écosystèmes indispensables à la digestion, à l'immunité ou au développement des intestins. Du reste, certains scientifiques voient dans les bactéries un organe à part entière. Au total, il y en aurait... un million de milliards dans le corps d'un adulte. Moins chez l'enfant, car la diversité et le nombre de bactéries augmentent avec le vieillissement de l'organisme et les contacts avec l'environnement, l'alimentation, etc.
M.-C.M. - SCIENCE & VIE QUESTIONS RÉPONSES N°6 > Janvier > 2011 |
|
Le Corps Humain Contient Davantage de Bactéries que des Cellules |
 Nous sommes composés au bas mot à 90 % de bactéries ! Le corps d'un adulte compte en effet quelque 75.000 milliards de cellules, contre plus de 10 fois plus de bactéries.
Nous sommes composés au bas mot à 90 % de bactéries ! Le corps d'un adulte compte en effet quelque 75.000 milliards de cellules, contre plus de 10 fois plus de bactéries.
La proportion est moins élevée chez l'enfant, car la diversité et le nombre de bactéries augmentent lorsque l'organisme vieillit, par contact avec l'environnement, l'alimentation, etc.. Plusieurs milliers d'espèces élisent ainsi peu à peu domicile dans le corps humain et y constituent de véritables écosystèmes, indispensables à la digestion, à l'immunité, au développement des intestins. Certains scientifiques tendent même à les considérer comme un organe à part entière. La plus grande partie de bactéries s'installe dans l'appareil digestif, mais on en trouve aussi dans toutes les parties du corps ouvertes sur l'extérieur : peau, yeux, nez, vagin...).
M.-C.Ma. - SCIENCE & VIE > Août > 2010 |
|
|
Toutes nos Bactéries vont être Recensées |
GÉNÉTIQUE |
Elles sont des milliards à peupler notre corps pour le meilleur et pour le pire. En décryptant notre profil bactérien, les chercheurs espèrent dessiner une nouvelle carte d'identité biologique de l'humanité.
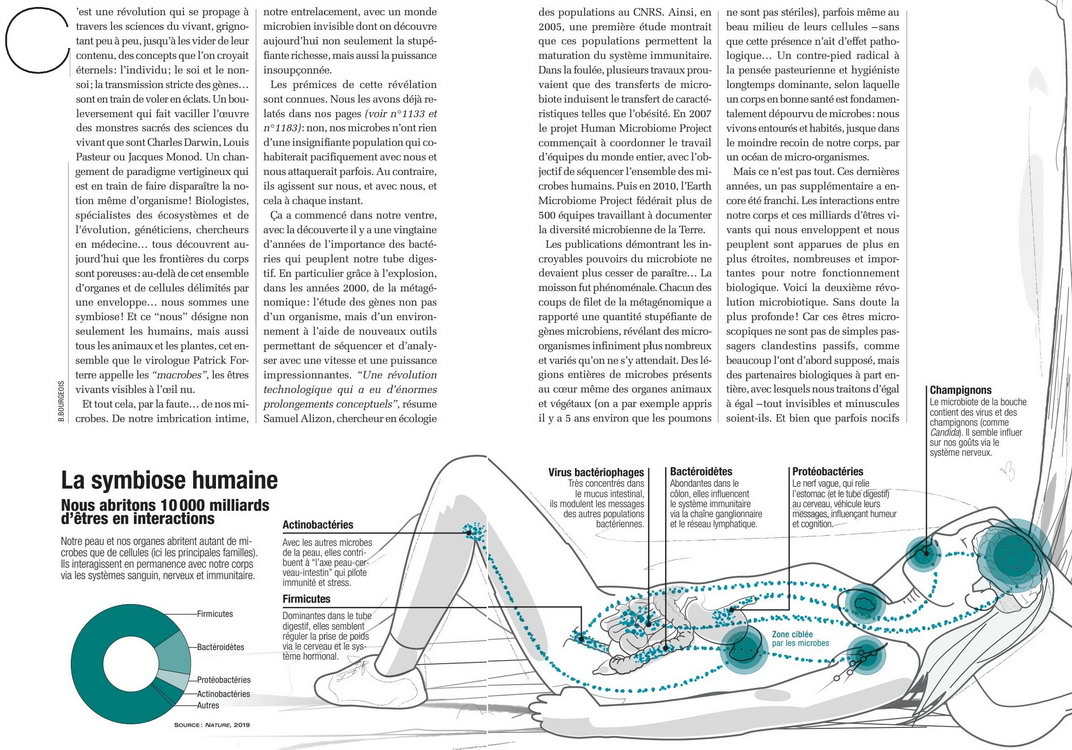
Qui sommes-nous ? Face à cette question, tout le monde a sa petite idée. Et la science n'est pas en reste puisque, grâce au décryptage du génome humain, elle dote désormais chacun d'un profil génétique qui lui est propre. À première vue, difficile d'aller plus loin... Et pourtant si ! Car notre corps héberge des centaines de milliards de bactéries qui pourraient aboutir à une carte d'identité attribuant cette fois à chacun d'entre nous un profil génétique bactérien. Les bactéries ? Si ces minuscules organismes vivants unicellulaires ne représentent que 1 à 2 % de notre masse totale, ils sont cinq à dix fois plus nombreux que nos cellules, jouent un rôle majeur dans notre bien-être et notre santé, et sont répartis un peu partout : la peau, la bouche, le nez, la gorge, les poumons, l'appareil génital... le plus grand réservoir étant toutefois le tube digestif. Et cette flore abondante pourrait fortement varier d'un individu à un autre. "Pourrait", car malgré leur nombre et leur importance pour notre organisme, ces bactéries demeurent largement méconnues, étant les grandes oubliées de la biologie moléculaire et de la médecine de ces dernières années.
Mais les choses vont changer. À travers le monde, un grand mouvement s'enclenche actuellement pour mieux connaître cet univers mystérieux et pourtant si proche. Objectif affiché : avoir fait en 2012 l'inventaire complet des patrimoines génétiques du petit millier (au bas mot) d'espèces bactériennes qui nous habitent, encore inconnues pour la plupart (voir ci-dessus). Autrement dit, avoir séquencé ce qu'on appelle notre métagénome (ou microbiome). Un travail de titan : selon les estimations, ce métagénome représenterait au moins 2,5 millions de gènes. Soit cent fois plus que notre génome qui, lui, plafonne à 20.000 gènes environ.
L'enjeu est de taille quand 95 % de ces bactéries nous seraient en réalité largement bénéfiques. Mieux : sans bactéries, il n'y aurait point d'humains sur cette terre. "Certaines nous aident à digérer ce que nous mangeons, et notamment les sucres et fibres de certaines plantes, que nous ne pourrions pas dégrader faute de disposer des enzymes nécessaires ; d'autres synthétisent de précieuses vitamines, comme la vitamine K", rappelle Dusko Ehrlich, directeur de recherches à l'lnstitut national de la recherche agronomique (Inra) et coordinateur du projet MetaHIT (Metagenome of Human Intestinal Tract). Comment toutes ces bactéries influent-elles sur notre état de santé ? Les différences dans les communautés bactériennes que nous abritons (notre profil bactérien) peuvent-elles expliquer des différences individuelles dans notre état de santé ? Et dans ce cas, quels sont les liens exacts entre notre métagénome et notre génome ?
Pour répondre à ces questions, un simple recensement des espèces bactériennes ne suffit pas : il faut aller plonger à l'échelle de leurs gènes. Les Européens se sont lancés dans la course les premiers. Leur projet MetaHIT, qui cible les bactéries de notre tube digestif, a démarré en avril 2008. Une belle longueur d'avance sur les Américains qui espèrent démarrer leur Human Microbiome Project en 2009. Ce projet, sorte de pendant bactérien du célèbre Human Genome Project, répartira ses efforts sur plusieurs régions clés du corps : la peau, le nez, la bouche, le pharynx, le tube digestif et l'appareil urogénital féminin. Au final, les chercheurs travailleront au sein d'un consortium international impliquant aussi la Chine, l'Australie et le Canada. Car la tâche est immense : "Il est essentiel de comprendre comment les micro-organismes interagissent avec le corps humain pour affecter la santé et les maladies, explique Elias A. Zerhoulil, le directeur des NIH (Institut national de la Santé américain). Ce projet a le potentiel de transfonner la manière dont nous concevons la santé, et de prévenir, diagnostiquer et traiter un large spectre de situations."
DEUX FAÇONS DE SÉQUENCER
Un enthousiasme partagé par nombre de scientifiques à travers le monde. "Il faut découvrir quelles communautés bactériennes vivent dans les différentes parties de notre corps et explorer comment leur présence joue sur notre santé et nos maladies", ajoute Francis Collins, le directeur du National Human Genome Research Institute, le pendant américain du Genoscope. Parmi les objectifs : déterminer si oui ou non nous partageons un noyau commun de métagénome. "A terme, l'idéal serait de connaître le profil bactérien de chaque personne, comme on connaît son génome, renchérit Dusko Ehrlich. Cela apporterait des informations sur son état de santé et sa sensibilité aux maladies. Mais aussi sur sa réponse aux médicaments - vitesse et taux d'absorption dont dépendent en partie l'efficacité et la propension à développer des effets non souhaités - et aux compléments alimentaires."
Pour mener à bien cet ambitieux projet, rendu possible par les avancées des technologies de séquençage de l'ADN, deux méthodes complémentaires seront employées. La première, relativement nouvelle, se concentre sur le séquençage des métagénomes proprement dits, c'est-à-dire les génomes de communautés bactériennes entières récupérées sur des volontaires anonymes. Le 2 juin 2006, dans la revue Science, le biologiste américain Steven Gill (université de Buffalo) fut ainsi le premier à publier le résultat du séquençage de deux métagénomes digestifs humains, celui d'un homme et celui d'une femme, à partir d'échantillons prélevés sur leurs selles. Oui, mais il n'est parvenu à isoler, respectivement, que 65.059 et 74.462 séquences. "Un an et demi plus tard, en décembre 2007, l'équipe japonaise de Masahira Hattori a réussi à séquencer plus d'un million de séquences, soit 600.000 gènes !", s'enthousiasme Dusko Ehrlich. Reste qu'aussi belle soit la performance, cette technique permet seulement d'analyser des cas individuels, et pas d'établir de grands profils bactériens.
La deuxième technique, elle, est plus ambitieuse puisqu'elle vise à identifier tous les gènes impliqués et les cascades biologiques qui en découlent via la mise en culture de chacune des mille espèces bactériennes qui nous colonisent, avant de procéder au séquençage systématique de leurs génomes. Mais il y a un problème : à ce jour, on ne sait cultiver en laboratoire qu'environ 30 % des bactéries. Avant de passer au séquençage génomique, il faudra donc dépasser cette étape. Il n'empêche, depuis quelques années, plusieurs résultats ont déjà montré que des variations dans la composition des communautés bactériennes peuvent contribuer à certaines affections chroniques, à des désordres digestifs et même à l'obésité. En plus des prédispositions génétiques et du mode de vie, le métagénome aurait-il donc un impact sur la prise de poids ? Deux études, publiées dans Nature en décembre 2006 et réalisées par Jeffrey Gordon et son équipe du Centre des sciences du génome de l'université Washington, à Saint-Louis (Missouri) le suggèrent. La première montre que la flore intestinale de personnes souffrant d'obésité contient de manière prédominante un certain type de bactéries, les Firmicutes. Or, les faire maigrir réduit le nombre de ces Firmicutes, au profit d'un autre type de bactéries, les Bacteroidetes - mais on ignore pour l'instant comment... Plus surprenant encore : la deuxième étude a révélé que transférer la flore intestinale de souris obèses à des souris minces les fait... grossir ! En fait, les Firmicutes accroîtraient nos capacités d'extraction calorique, comme semblent l'indiquer les mesures calorimétriques réalisées sur les selles des souris.
Et ce n'est pas tout. D'autres maladies, comme l'asthme, les allergies ou les maladies auto-immunes, pourraient également être sous l'influence de bactéries. C'est la théorie de Martin Blaser, professeur de microbiologie à l'Ecole de médecine de l'université de New York. Selon lui, certains agents pathogènes, tel Helicobacter pylori, qui provoque ulcères et cancers de l'estomac, peuvent aussi s'avérer bénéfiques. "Plusieurs études suggèrent que cette bactérie pourrait avoir un effet protecteur contre l'asthme chez les enfants (40 % de risque en moins), sur les allergies aux pollens et aux moisissures, et même sur certains cancers osophagiens", explique-t-il. Et il pourrait aussi y avoir un lien entre la présence de H. pylori et le maintien en phase de latence de la tuberculose, maladie causée par une autre bactérie, Mycobacterium tuberculosis. C'est en tout cas ce que relève une étude menée par Shanon Perry et Julie Parsonnet, de l'université de Stanford, présentée en octobre 2007 au 45ème Congrès annuel de la Société américaine des maladies infectieuses.
HARO SUR LES ANTIBIOTIQUES
Toutes ces observations apportent du grain à moudre aux tenants de la vieille théorie selon laquelle l'exposition aux infections microbiennes (bactéries, virus) stimule notre système immunitaire et l'empêche de se retourner contre nous. Resterait à choisir entre ne pas faire un ulcère en éliminant H. pylori mais courir le risque de souffrir d'asthme ? "Il faut avoir une vision plus complexe de ces organismes. Leur présence entraîne des coûts et des bénéfices, variables selon les personnes, souligne Martin Blaser, qui s'inquiète de l'usage massif des antibiotiques. H. pylori a été l'organisme dominant dans notre estomac pendant des milliers d'années. Il ne peut pas disparaître sans conséquences. A cause des traitements anti-biotiques répétés chez les enfants, nous sommes en train de changer la microécologie humaine. Nous ne savons pas ce que nous faisons". Même son de cloche du côté de Steven Gill. Selon lui, l'absence ou la présence de certaines bactéries, ou même un changement dans leur population, peut déclencher des dysfonctionnements dans notre métabolisme et le développement de pathologies. "Nous avons évolué, ou plutôt co-évolué, avec ces microbes, et notre bien-être en dépend entièrement", explique-t-il. Avant de déclarer sans ambages : "Il sera impossible d'obtenir un tableau complet de notre biologie si l'on ne comprend pas les interactions entre les génomes humains et bactériens. Notre identité génétique complète est un mélange entre des gènes humains et des gènes bactériens."
A peine commencés, les programmes MetaHIT et Human Microbiome Project se voient donc presser de répondre à ces deux grandes questions : l'usage excessif des antibiotiques est-il en train de bouleverser l'équilibre de notre flore indispensable ? Et serait-il possible de modifier cet équilibre afin de guérir des malades ? Rendez-vous dans cinq ans.
QUELQUES HABITANT DU CORPS HUMAIN
On estime à environ 1 millier le nombre d'espèces bactériennes qui nous "peuplent". Ce chiffre est notamment basé sur des observations microscopiques et des méthodes de biologie moléculaire. Beaucoup de ces espèces, surtout les plus rares (celles dont la proportion est inférieure à moins de 1/‰) sont encore inconnues. Voici quelques-unes des familles bactériennes connues.
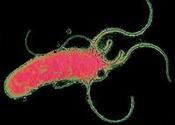 HELICOBATER PYLORI
HELICOBATER PYLORI
LOCALISATION - Muqueuses de l'estomac
RÔLE DANS l'ORGANISME - Globalement pathogène, cette bactérie provoque des ulcères et parfois même des cancers de l'estomac. Elle s'installe dans les muqueuses de notre estomac généralement avant nos 10 ans, et peut y perdurer pendant des décennies. Cependant, il semble qu'elle ait aussi le pouvoir de minimiser les risques d'asthmes, d'allergies, de maladies auto-immunes et de cancers osophagiens. En raison de l'usage massif des antibiotiques, sa prévalence a récemment beaucoup diminué dans les pays développés.
 STAPHYLOCOCCUS EPIDERMIS
STAPHYLOCOCCUS EPIDERMIS
LOCALISATION - Peau, nez, bouche, gorge
RÔLE DANS l'ORGANISME - Cette bactérie commensale recouvre la peau (concentration de 100 à 1 million de bactéries par cm²). Elle empêche les bactéries pathogènes de s'installer (comme Staphylocoque doré). Cependant, en cas d'immunodépression, de poses de cathéters, de prothèses, elle peut devenir pathogène. Elle cohabite avec les corynébactéries, responsable des odeurs corporelles, et partage son habitat avec S. capitis, présente sur le cuir chevelu, et S. auricularis, retrouvée dans le conduit auditif externe.
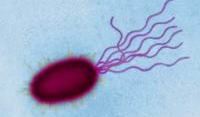 ESCHERICHIA COLI
ESCHERICHIA COLI
LOCALISATION - Habituellement, intestin grêle et côlon
RÔLE DANS L'ORGANISME - E. coli est largement bénéfique.
Elle nous aide à digérer certains sucres et fibres, empêche les bactéries pathogènes de se développer dans notre tube digestif, tandis que certaines souches synthétisent la vitamine K. cependant, la souche 0157: H7 est à l'origine d'épidémies mortelles.
 BACTÉROÏDE Thetaiotaomicron - Methanobrevibacter smithii
BACTÉROÏDE Thetaiotaomicron - Methanobrevibacter smithii
LOCALISATION - Habituellement, intestin grêle et côlon
RÔLE DANS L'ORGANISME - Ces 2 bactéries interagissent pour modifier nos capacités d'extraction caloriques des aliments. Des expériences ont montré qu'en recevant la même quantité de nourriture, les souris à qui ont a inoculé M. smithii (une archéobactérie) et B. thetaiotaomicron voient leur masse graisseuse augmenter de plus de 50 % par rapport aux souris à qui l'on a seulement inoculé B. thetaiotaomicron. M. smithii modifierait le comportement de B. thetaiotaomicron en améliorant son utilisation de certains sucres abondants.
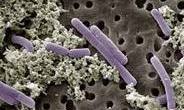 LACTOBACILLUS CASEI
LACTOBACILLUS CASEI
LOCALISATION - Intestin grêle, côlon
RÔLE DANS L'ORGANISME - La très médiatique souche DN-114 001 de L. casei a été baptisée "Defensis" par Danone, qui l'utilise comme argument marketing.
Elle réduirait la fréquence et la durée des diarrhées aiguës chez les jeunes enfants. Le génome entier de L. casei vient d'être séquencé par le Génoscope d'EVry, l'Inra et Danone.
R.P. - SCIENCE & VIE > Mai > 2008 |
|